W.Si bien CRISPR puede ser la tecnología genética más notable que surge de los microbios, muchas de las herramientas que utilizan los investigadores para controlar los genes y sus productos se toman prestadas de sistemas bacterianos. Uno de estos es el laca operón, que regula la expresión de genes implicados en el metabolismo de la lactosa en Escherichia coli. Aplicaciones desde mesas de laboratorio hasta cubas industriales utilizan esto para activar selectivamente la expresión genética.
Sin embargo, en la mayoría de los casos, los investigadores sólo han tomado prestada una parte de la información. laca sistema de operones. Utilizan la proteína represora, LacI, que une físicamente el ADN aguas arriba del promotor del gen para bloquear la ARN polimerasa, luego agregan una molécula inductora que eliminará LacI cuando los investigadores quieran activar la expresión genética. Si bien este sistema diseñado regula la expresión de genes, requiere altas concentraciones de LacI para reprimirlos consistentemente.1 En comparación, la forma completa del operón que ocurre en Escherichia coli incluye sitios de unión adicionales para LacI que forman un bucle de ADN, reprimiendo más eficientemente la transcripción del laca genes de operón que utilizan menos proteína represora.
Un equipo está interesado en aprovechar esta característica para desarrollar un nuevo enfoque para la regulación genética. En un estudio publicado en Investigación de ácidos nucleicosinvestigadores de la Clínica Mayo crearon una nueva proteína que imitaba la capacidad de doble unión de LacI, ofreciendo un nuevo enfoque para regular la expresión genética en el futuro.2
LacI es una proteína tetramérica que utiliza dos dímeros para unir dos secuencias de ADN idénticas y específicas. Esta especificidad reduce la capacidad de utilizar el sistema LacI en los casos en que los investigadores no pueden insertar esta secuencia, lo que lleva a la búsqueda de una proteína represora más flexible que pueda reconocer más regiones del ADN.
“Probablemente fue alrededor de 2015 cuando comenzamos a trabajar en la idea de un circuito de represión genética más diseñado”, dijo Nicole Beckerbiólogo molecular de la Clínica Mayo y coautor del estudio.
proteínas CUENTOabreviatura de efector similar al activador de la transcripción (TALE), son una clase de proteínas derivadas de patógenos vegetales en el xantomonas género.3 Los TALE reconocen el ADN mediante una serie repetitiva de 34 regiones de aminoácidos en las que los 12th y 13th El aminoácido determina el ácido nucleico al que se unirá cada segmento. Los patógenos utilizan estas proteínas para activar la expresión genética en las plantas que promoverá la supervivencia de las bacterias, pero los científicos agrietado este código de unión al ADN para crear TALE personalizados que puedan reconocer cualquier secuencia a la que quieran apuntar.4,5
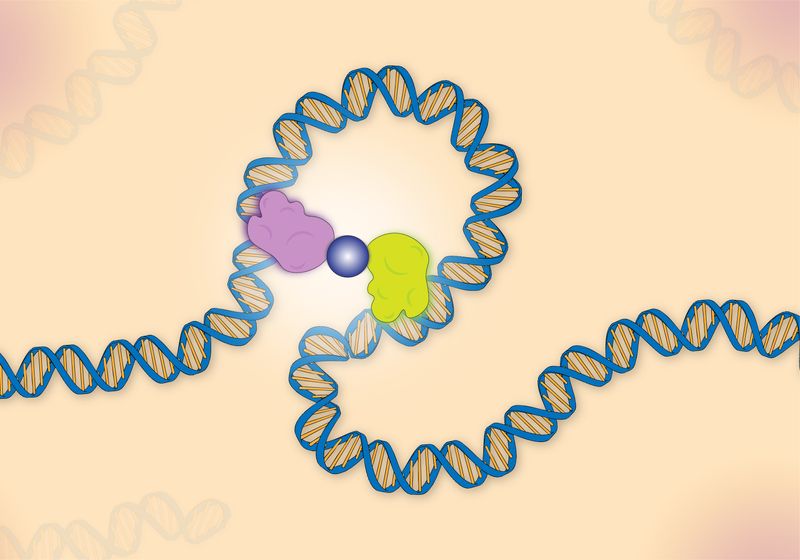
En el presente estudio, el equipo copió la naturaleza bicéfala de LacI uniendo dos dímeros TALE diferentes, denominados A y O.2que reconocen distintas secuencias de ADN. Insertaron estas dos secuencias aguas arriba de un gen indicador y utilizaron un ensayo colorimétrico para determinar si las proteínas reprimieron la expresión del indicador basándose en la ausencia de color. Su objetivo era determinar los parámetros necesarios para lograr una represión genética comparable a la de LacI.
En primer lugar, el equipo evaluó el efecto que tenía el orden de los dos dímeros TALE de la proteína sobre la eficacia de la represión. Investigaciones anteriores indicaron que colocar el represor más fuerte más lejos del promotor mejoró la represión, por lo que probaron el grado de represión de A y O2.6 Luego, insertaron la secuencia para el TALE A más fuerte en el sitio distal de su promotor y el TALE O más débil.2 más cerca de la secuencia de inicio.
El equipo estudió los parámetros óptimos del dímero utilizando modelos matemáticos de unión y represión de proteínas. Determinaron que diseñar el dímero con TALE A como el primer TALE en la secuencia de aminoácidos y TALE O2 ya que el segundo creó un dímero más represivo que lo contrario.
Finalmente, el equipo comparó la represión de su dímero TALE con LacI. El dímero TALE covalente se desempeñó de manera comparable a LacI según su modelado. “Ahí fue realmente donde se volvió intrigante que pudiéramos crear artificialmente algo que pudiera crear un bucle de ADN que fuera tan fuerte como el que se podía ver en el sistema represor lac”, dijo Becker.
“Es una aplicación muy inteligente de TALE”, dijo Adam Bogdanovepatólogo de plantas moleculares de la Universidad de Cornell que no participó en el estudio. El grupo de Bogdanove fue uno de los equipos que describió originalmente el código de secuencia de TALE. Dijo que el trabajo experimental y de modelado era un buen enfoque para optimizar las proteínas y explorar sus funciones. “Es otra herramienta poderosa en la caja de herramientas para moderar o manipular la expresión genética con el fin de comprender la función genética”, dijo.
Una comparación que Bogdanove dijo que sería interesante ver en el futuro fue la eficacia con la que los dímeros TALE reprimen la expresión genética en comparación con los sistemas de interferencia CRISPR. Además, dijo que mejorar el sistema de dímeros para que se pueda regular el grado de represión ayudaría a ampliar su aplicación.
Becker y sus colegas también están interesados en explorar formas de hacer que el sistema sea sintonizable, así como en estudiarlo en modelos eucariotas. A diferencia de LacI, se puede hacer que las proteínas TALE reconozcan cualquier secuencia. Explicó que su equipo utilizará los parámetros que identificaron para probar este mecanismo de represión del dímero TALE contra nuevas regiones del ADN en bacterias y eucariotas.